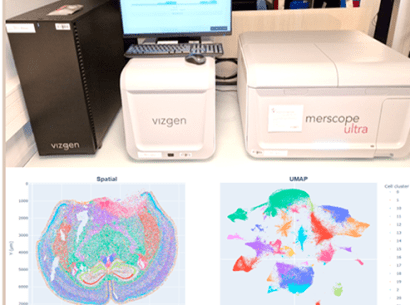
L’équipe Sysfate (Unité de Génomique métabolique – Genoscope), dirigée par Marco Mendoza, a mis au point une méthode de cartographie tridimensionnelle de l’activité biologique des tissus, utile à la compréhension de la complexité des organes, ainsi qu’à l’étude de leur développement ou de l’impact des maladies. L’équipe applique son système de puces à ADN à double code-barre moléculaire et ses outils bio-informatiques à la technique de transcriptomique spatiale, réduisant ainsi drastiquement son coût et ses limites.
Marco Mendoza a crée, fin 2018, son équipe Sysfate afin d’explorer les mécanismes moléculaires de la neurogenèse.
Il a bénéficié pour cela du programme financier Atige de Genopole, du soutien de l’Université d’Evry et d’équipements scientifiques mis à disposition par Genopole et Télécom Sud Paris.
En 2021, l’équipe a conçu l’outil Multilayer qui, à partir de données de transcriptomique spatiale*, produit des cartes en deux dimensions de l’activité biologique d’organes ou de tissus, comme les tissus tumoraux, cardiaques, etc.
A partir de coupes transversales de tissus, la méthode peut fournir une image rendant compte de l’expression d’un millier de gènes en des centaines de localisations sur le tissu, chaque point correspondant à un ensemble de cellules.
Dans une publication dans Cell Reports Methods en automne 2023, l’équipe a franchi un nouveau cap en parvenant à digitaliser en 3 dimensions des organoïdes, structures multicellulaires reproduisant les tissus cérébraux, produites en laboratoire. La méthode développée par les chercheurs évryens consiste à analyser des coupes successives des organoïdes cérébraux à l’aide d’un système de puces à ADN et établir une cartographie 3D du niveau d’expression des gènes.
L’approche repose sur des avancées technologiques réalisées par l’équipe génopolitaine sur deux axes complémentaires :
- La conception d’un système de double code-barre ADN qui assure l’identification précise de la localisation dans l’espace de chaque point du tissu, avec un nombre limité de sondes ADN.
En effet, la limite majeure à la transcriptomique 3D est le très grand nombre de sondes ADN nécessaire pour marquer chaque point du tissu.
Là où il fallait plus de 1 000 sondes pour couvrir la surface des organoïdes, la solution développée par l’équipe génopolitaine ne nécessite que 2 séries de 32 sondes, soit 64 sondes : l’espace est quadrillé ; la première série de sondes repère la position « Ligne » et la seconde la position « Colonne »; la combinaison des deux révèle 32 x 32 positions, soit 1024 positions ! - L’exploitation des technologies de séquençage ADN de dernière génération et les développements bio-informatiques d’analyse de ces données de séquençage, afin de reconstituer une image tridimensionnelle qui révèle les différences d’expression génique dans le tissu. Les outils identifient également les zones de co-expression des gènes, et découpent ainsi le tissu en sous-structures à l’activité moléculaire similaire.
L’équipe a notamment exploré l’utilisation de la technologie de séquencage « Nanopore » pour la transcriptomique spatiale en participant au Hackathon D4Gen (Digital for Genomics) organisé par Genopole.
Les chercheurs évryens ont révélé ainsi (cf. figure ci-dessous), sur des organoïdes cérébraux obtenus après des mois de culture au laboratoire et divisés en 15 coupes transversales, l’expression de 4000 gènes par point de lecture (appelé gexel en référence aux pixels des images numérisées), soit plus du double de ce qui est atteint avec les sondes actuellement commercialisées.
Ils ont pu ainsi identifier dans les organoïdes 24 sous-structures tissulaires avec des signatures d’expression génique proche de tissus cérébraux connus comme l’épithélium neuronal ou le cortex cérébral fœtal. La méthode a permis aussi d’étudier individuellement la surexpression de plusieurs gènes d’intérêt dans le tissu (sur la figure, exemple du gène CNTNAP2) et de valider les données par la méthode d’immunofluorescence (CASPR2) dans les sections consécutives de tissus.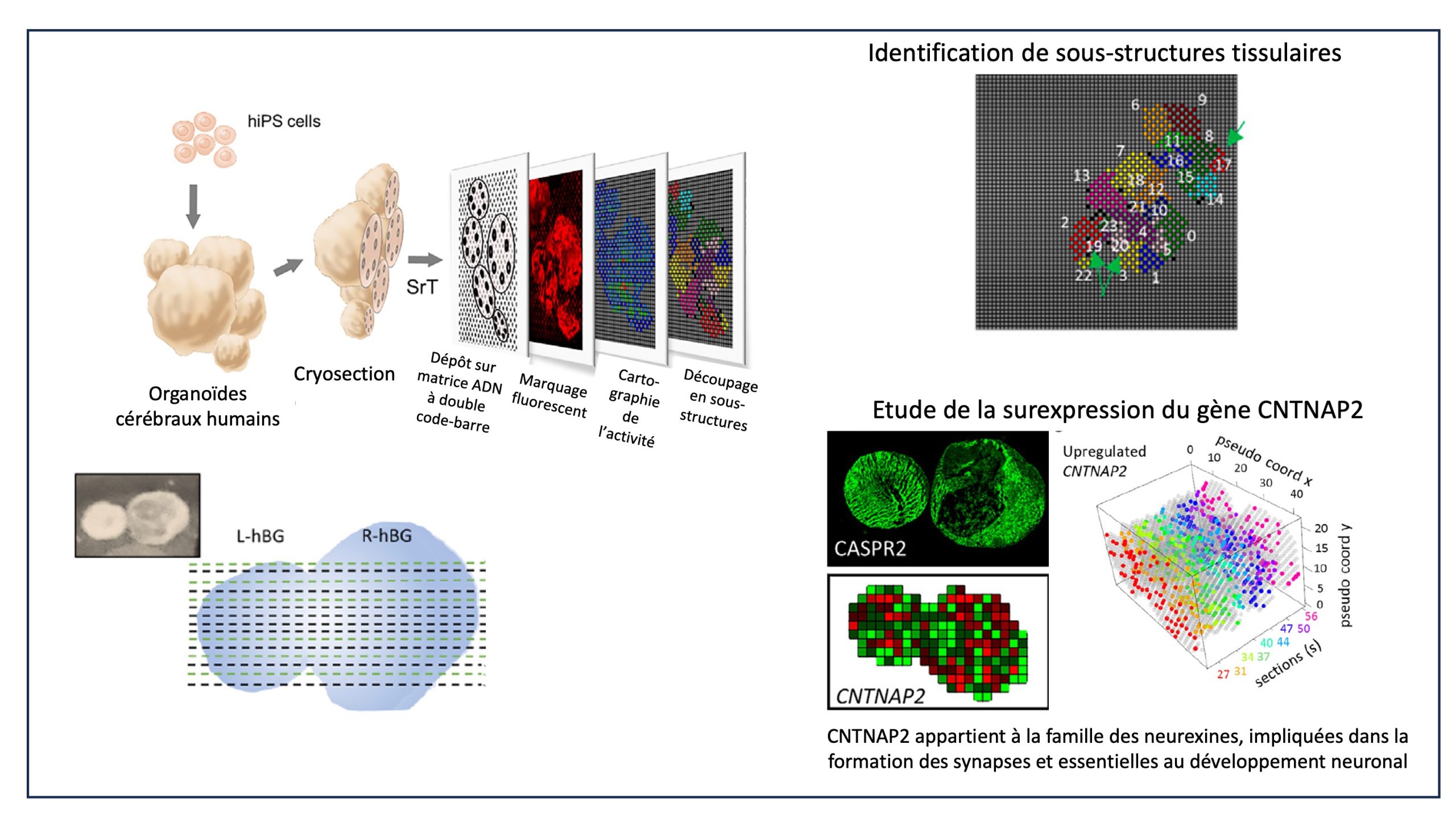



 Marco Mendoza (ici dans son laboratoire) a bénéficié du soutien de Genopole pour l’
Marco Mendoza (ici dans son laboratoire) a bénéficié du soutien de Genopole pour l’